295: 核醣體多樣性(Ribosome Diversity)
2000年首次確定的核糖体(ribosome)原子結構揭示了生物蛋白質合成的細節。核醣體的小亞基負責管理信使 RNA,將其與適當的轉運RNA( transfer RNA)分子配對,並使密碼子與反密碼子相匹配。核醣體的大亞基將轉運RNA攜帶的胺基酸連接成新的蛋白質鏈。在這項發現之後的25年中,又有數千個核醣體結構被成功解析,許多蛋白质合成的步骤也被闡明。這些結構也使得比較不同生物的核醣體結構成為可能。
不斷演變的複雜性
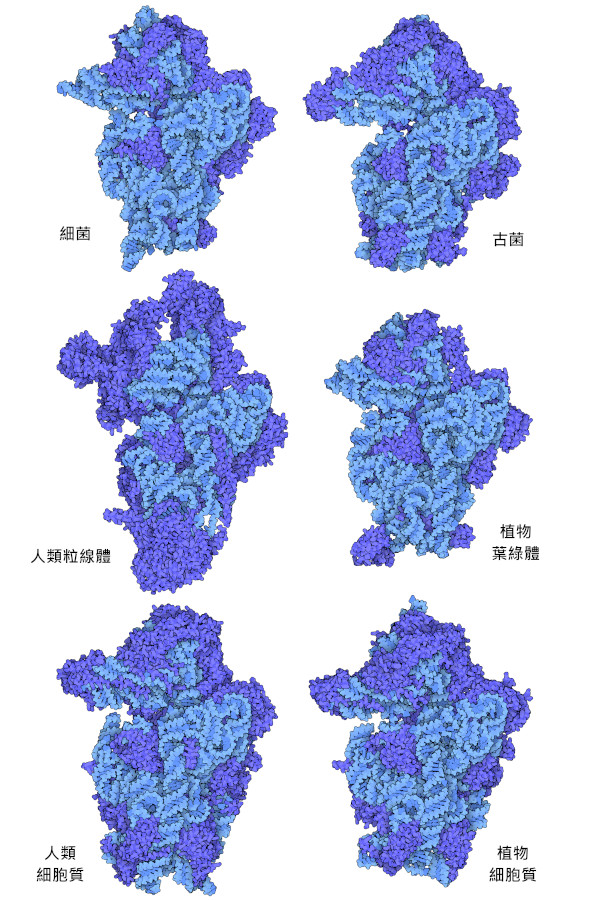
由於功能性核醣體對所有生物都是必需的,因此核醣體的結構對研究分子演化非常有用,並且可以對所有生物的核醣體進行比較。這裡的圖片展示了幾種不同生物的核醣體小型亞基。細菌的核醣體結構相對簡單,小亞基(PDB ID 1fjg)包含一條長度為1522個核苷酸的 RNA 鍊和 20 個蛋白質。同樣,古細菌小亞基(PDB ID 6tmf)也有一條長度為 1485 個核苷酸的小 RNA 鍊和 29 個蛋白質。相較之下,人類和植物中的小亞基(PDB ID 5a2q, 8auv)的結構更為複雜,其 RNA 鍊長度超過 1800 個核苷酸,蛋白質超過 30 種。
攜手合作
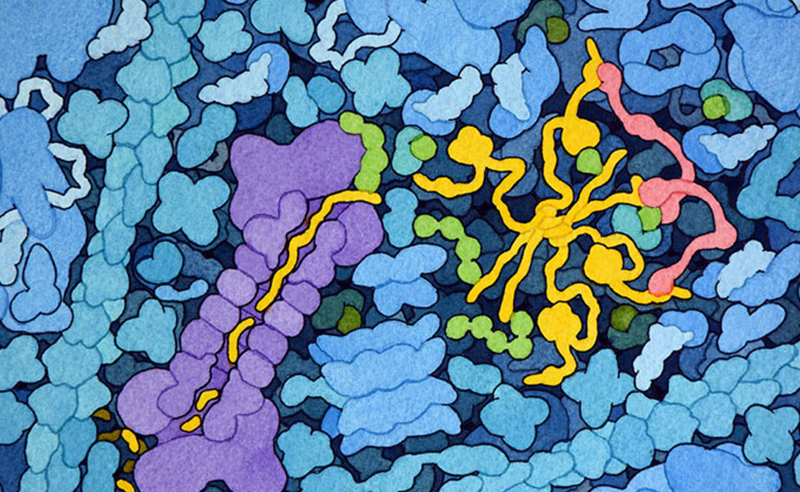
粒線體(mitochondria)和葉綠體(chloroplast)製造自己的核醣體,與植物、動物和真菌細胞質中的核醣體不同。這兩種細胞器都被認為是從細菌演化而來的,這些細菌在現代真核細胞祖先的細胞質中共生。葉綠體核醣體的結構是支持這種內共生假說的證據之一。葉綠體核醣體的小型亞基(PDB ID 5mmj)與細菌核醣體的小亞基相似,由長度為 1491 個核苷酸的短 RNA 和25 個蛋白質組成。粒線體核醣體的小亞基(PDB ID 6rw4)的結構表明,粒線體核醣體與與其假定的細菌前身有顯著差異,與細菌核醣體相比,粒線體核醣體的 RNA 鏈更短,只有 955 個核苷酸,蛋白質含量比典型的細菌核醣體更多。
啟動的複雜性
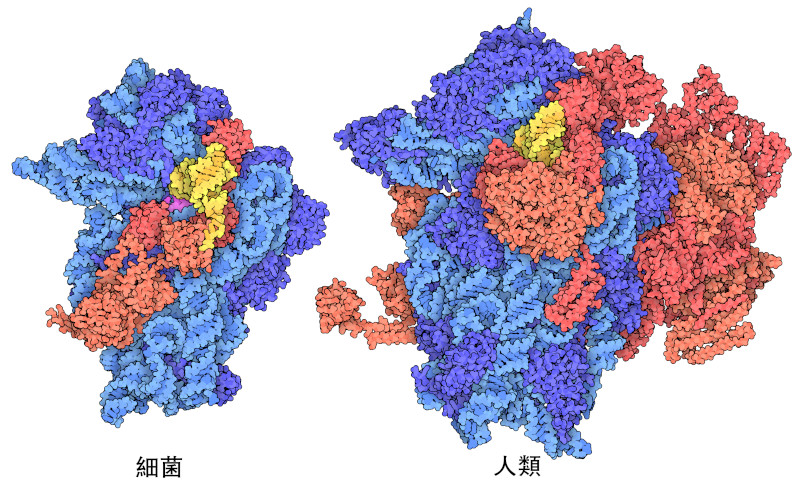
真核生物的複雜性也體現在協助核醣體進行蛋白質合成的許多蛋白質。例如,這裡顯示的兩個結構(PDB ID 5lmv, 8oz0)代表了協調蛋白質合成啟動的蛋白質。它們一起幫助捕獲信使 RNA,並將起始轉運RNA與翻譯起始密碼子對齊。細菌細胞只需要三個起始因子蛋白就能完成這項任務,而真核生物則需要大約 20 個。
探索結構
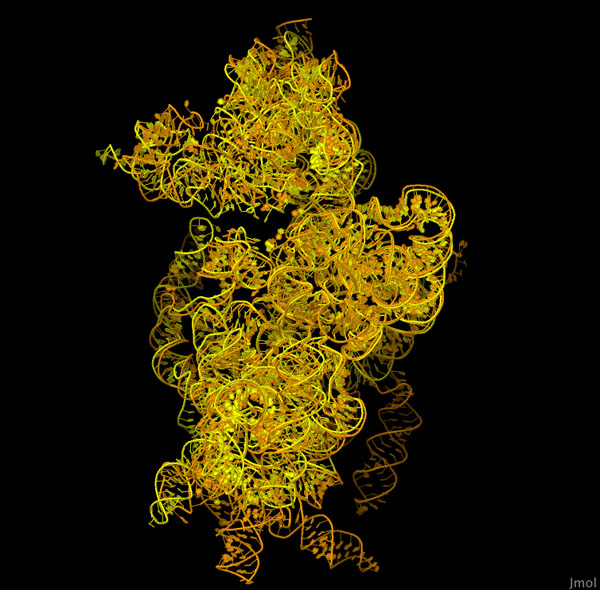
若要切換到有互動控制的頁面,請點選圖表下方的按鈕。如果載入沒有開始,請嘗試點擊圖表。
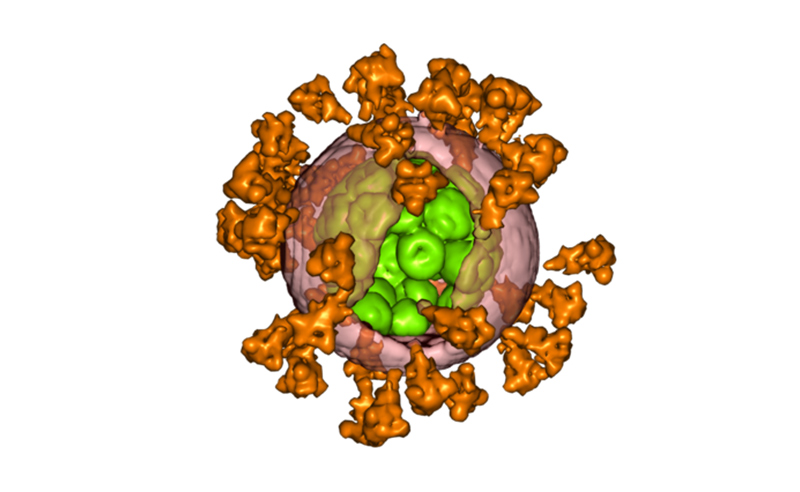
此交互視圖比較了來自細菌和人類小亞基(PDB ID 1fjg, 5a2q)的核醣體 RNA。請注意,這兩種結構都有一個相似的核心,它的基本任務是將信使 RNA 和轉運RNA結合在一起。就人類 RNA 而言,圍繞著這一核心有許多延伸部分,從而形成更大、更複雜的核醣體亞基。點擊圖片下方的按鈕,切換到互動模式,更詳細地了解這些結構。
進一步的討論議題
參考文獻
- 8oz0 2024 The structure of a human translation initiation complex reveals two independent roles for the helicase eIF4A. Nat Struct Mol Biol 31 455-464
- 8auv 2023 Structure of the actively translating plant 80S ribosome at 2.2 angstrom resolution. Nat Plants 9 987-1000
- 6rw4 2020 Distinct pre-initiation steps in human mitochondrial translation. Nat Commun 11 2932-2932
- 6tmf 2020 Molecular analysis of the ribosome recycling factor ABCE1 bound to the 30S post-splitting complex. EMBO J 39 e103788
- 5mmj 2017 The complete structure of the chloroplast 70S ribosome in complex with translation factor pY. EMBO J 36 475-486
- 5lmv 2016 Large-scale movements of IF3 and tRNA during bacterial translation initiation. Cell 167 133-144.e13
- 5a2q 2015 Cryo-EM structure of hepatitis C virus Ires bound to the human ribosome at 3.9 Angstrom Resolution. Nat Commun 6 7646
- 1fjg 2000 Functional insights from the structure of the 30S ribosomal subunit and its interactions with antibiotics. Nature 407 340-348
 生物大分子學習的教育門戶
生物大分子學習的教育門戶